- 软件gydF4y2Ba
- 开放获取gydF4y2Ba
- 发表:gydF4y2Ba
RSAtrace3D:用于测量单子叶植物根系结构的稳健向量化软件gydF4y2Ba
BMC植物生物学gydF4y2Ba体积gydF4y2Ba21gydF4y2Ba文章编号:gydF4y2Ba398gydF4y2Ba(gydF4y2Ba2021gydF4y2Ba)gydF4y2Ba
摘要gydF4y2Ba
背景gydF4y2Ba
根系在土壤中的分布是构成根系体系结构(RSA)的要素之一。在单子叶植物中,RSA由胚根和冠根组成,每根根基本上可以用一条带侧根分支的曲线表示,也可以用折线近似表示。此外,RSA向量化(折线转换)对RSA表型分型很有用。然而,一个健壮的软件可以启用RSA向量化,同时使用噪声三维(3D)体是不可用的。gydF4y2Ba
结果gydF4y2Ba
我们开发了RSAtrace3D,这是一个健壮的3D RSA向量化软件,用于单子代RSA表型分型。它将单根(根或冠根)作为折线(向量)进行管理,折线的集合表示整个RSA。RSAtrace3D向量化单个根两端之间的根段。通过利用根上的几个基点,RSAtrace3D适合噪声图像,如果仅使用根的两个端点节点很难向量化噪声图像。此外,通过使用一个简单的跟踪算法(使用根体素的重心(COG)来确定跟踪方向),RSAtrace3D可以有效地向量化根。因此,RSAtrace3D比直线或样条曲线更精确地表示单个根形状。作为一个案例研究,大米(gydF4y2Ba栽培稻gydF4y2Ba)从x射线计算机断层扫描(CT)图像向量化RSA,并计算RSA特征。此外,还观察到RSA性状的品种差异。向量数据比原始x射线CT图像紧凑32000倍。因此,这使得共享数据和执行重新分析更加容易。例如,使用以前进行的研究的数据。对于单子叶植物,向量化和表型分型算法是可扩展的,适用于许多应用。gydF4y2Ba
结论gydF4y2Ba
RSAtrace3D是一款用于单性状3D RSA表型分析的RSA向量化软件。由于RSA向量化和表型分型算法的高度可扩展性,RSAtrace3D不仅可以应用于X-ray CT图像中的水稻,还可以应用于各种3D图像中的其他单性状。由于该软件是用Python语言编写的,因此易于修改,将被该领域的研究人员广泛应用。gydF4y2Ba
背景gydF4y2Ba
作为构成根系统架构(RSA)的要素之一[gydF4y2Ba1gydF4y2Ba,gydF4y2Ba2gydF4y2Ba],根系在土壤中的分布决定了土壤对水分和养分的吸收有效性。这是因为植物可以在根部接触到的范围内吸收水分和养分。gydF4y2Ba3.gydF4y2Ba,gydF4y2Ba4gydF4y2Ba].因此,根系分布极大地影响作物产量[gydF4y2Ba5gydF4y2Ba].例如,浅根植物通过在靠近地表的地方施肥表现更好,而深根植物则通过在深层土壤区域施肥表现更好[gydF4y2Ba6gydF4y2Ba].在深根植物中,干旱引起的水分缺陷是可以避免的,因为它们的根系伸长到含有更多水分的土壤深处[gydF4y2Ba4gydF4y2Ba,gydF4y2Ba7gydF4y2Ba,gydF4y2Ba8gydF4y2Ba].gydF4y2Ba
由于RSA表型分型过程复杂而费力[gydF4y2Ba9gydF4y2Ba],与与产量明显相关的地上性状相比,RSA性状没有得到广泛的测量[gydF4y2Ba10gydF4y2Ba].RSA表型分型的另一个问题是,到目前为止,大多数之前进行的RSA研究都应用了二维(2D)信息[gydF4y2Ba10gydF4y2Ba,gydF4y2Ba11gydF4y2Ba].二维信息将不足以表示三维(3D)根系结构和在土壤中的部署。最近,3D RSA表型分型已经可以使用3D成像机器,如x射线计算机断层扫描(CT)、磁共振成像(MRI)和多摄像机系统[gydF4y2Ba11gydF4y2Ba,gydF4y2Ba12gydF4y2Ba,gydF4y2Ba13gydF4y2Ba,gydF4y2Ba14gydF4y2Ba].特别是x射线CT和MRI可以在原位观察土壤中的根系,并被广泛用于RSA研究[gydF4y2Ba15gydF4y2Ba].gydF4y2Ba
利用软件量化RSA特征,在x射线CT和MRI图像中分离根段。以x射线CT为例,RooTrak [gydF4y2Ba16gydF4y2Ba,gydF4y2Ba17gydF4y2Ba), RootViz3D®(gydF4y2Ba18gydF4y2Ba], Rootine [gydF4y2Ba19gydF4y2Ba]和RSAvis3D [gydF4y2Ba20.gydF4y2Ba]被开发为分割土壤中的根系的软件。基于根的形状和分支等结构信息,RooTrak和RootViz3D®通过从操作符指示的点开始跟踪根段来分离根段[gydF4y2Ba16gydF4y2Ba,gydF4y2Ba17gydF4y2Ba,gydF4y2Ba18gydF4y2Ba].此外,Rootine和RSAvis3D无需人工操作即可分离根段;根利用根的管状形状特征检测对根进行分段,RSAvis3D利用边缘检测算法对根进行分段[gydF4y2Ba19gydF4y2Ba,gydF4y2Ba20.gydF4y2Ba].以MRI为例,开发了nmroot软件[gydF4y2Ba21gydF4y2Ba].nmroot只是通过阈值方法分离根段[gydF4y2Ba21gydF4y2Ba].在此基础上,对分离的根段进行了RSA特征的测量。例如,通过根段的体素计数计算根体积[gydF4y2Ba16gydF4y2Ba,gydF4y2Ba17gydF4y2Ba,gydF4y2Ba18gydF4y2Ba],而根长度则由骨架化根段的体素计数近似而来[gydF4y2Ba19gydF4y2Ba,gydF4y2Ba22gydF4y2Ba].gydF4y2Ba
RSA向量化(连接相邻根体素以使路径表示RSA形状)是RSA表型分型的一种方法,允许进行拓扑分析和根生长角计算[gydF4y2Ba21gydF4y2Ba,gydF4y2Ba23gydF4y2Ba].在NMRooting的情况下[gydF4y2Ba21gydF4y2Ba],它具有3D向量化功能,RSA是通过跟踪从每个根体素到根-梢结点的最短路径向量化的,然后修剪不在根段上的短路径。然而,这种向量化算法对三维体中的噪声非常敏感。通常,在图像采集中,扫描时间、扫描区域大小和图像质量之间存在权衡[gydF4y2Ba24gydF4y2Ba,gydF4y2Ba25gydF4y2Ba,gydF4y2Ba26gydF4y2Ba,gydF4y2Ba27gydF4y2Ba].因此,快速扫描大尺寸罐容易产生噪声图像数据。此外,土壤中的矿物质、空气和水也会变成噪音[gydF4y2Ba26gydF4y2Ba].例如,在RSAvis3D上进行的一项研究中,根分割图像有很大的噪声[gydF4y2Ba20.gydF4y2Ba].这是因为RSAvis3D的条件是适用于高通量RSA可视化,因此优先考虑图像质量;它扫描了使用煅烧粘土的相对较大的罐子[gydF4y2Ba28gydF4y2Ba(粒子之间有很大的空隙)在短时间内。此外,从田间收集的未受干扰土壤样本的x射线CT图像[gydF4y2Ba29gydF4y2Ba]也包含非根段作为噪声。在这种情况下,需要一种具有不受噪声影响的鲁棒算法的向量化软件。gydF4y2Ba
在本研究中,基于RSAvis3D的根分割图像[gydF4y2Ba20.gydF4y2Ba,我们开发了一个鲁棒向量化软件RSAtrace3D来测量单子叶的RSA。RSAtrace3D通过指出一些表示根所在位置的基点,即使在噪声图像中也可以向量化包含根和冠根的单子叶RSA。此外,我们向量化大米(gydF4y2Ba栽培稻gydF4y2Ba),并测量与RSA相关的性状,如根系长度、根系生长角度和根系在土壤中的分布参数。我们证明,这些测量等于或更准确的执行使用手工或二维向量化。gydF4y2Ba
实现gydF4y2Ba
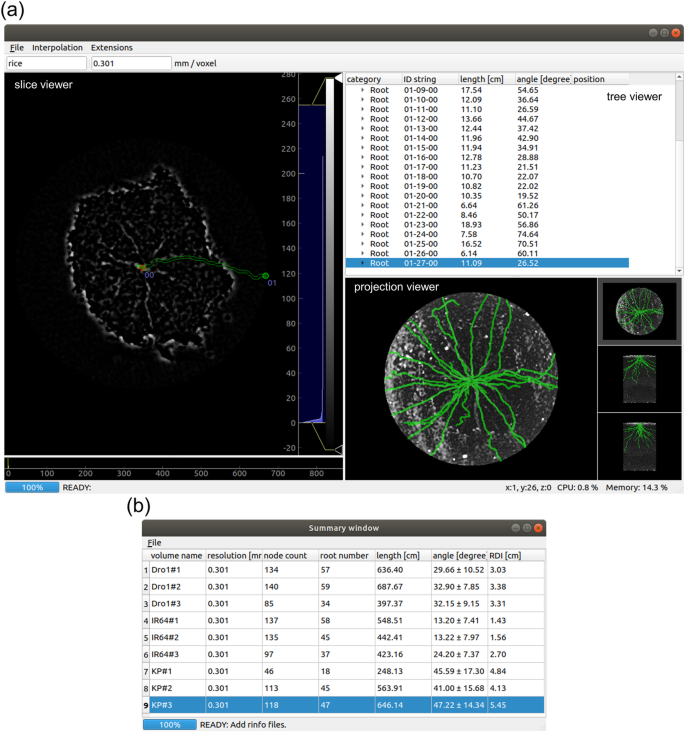
RSAtrace3D是一个用Python3实现的图形用户界面(GUI)软件[gydF4y2Ba30.gydF4y2Ba(图。gydF4y2Ba1gydF4y2Ba(a))。它有一个主窗口,包括三个子查看器(切片、树和投影查看器),用于显示操作人员处理的图像和数据,它使人们能够直观地操作CT图像分析。它显示由操作员在任意位置选择的卷切片图像。此外,RSAtrace3D需要基点在切片图像中进行向量化,操作符将它们作为切片查看器中的“节点”放置。因此,RSAtrace3D使用给定的节点向量化根,并计算单个根相关的特征。结果显示在树查看器中。投影查看器帮助我们观察向量化的总体进展。此外,向量化的RSA被保存为JavaScript对象表示法(JSON) [gydF4y2Ba31gydF4y2Ba格式化为“根信息(rinfo)”的文件。从rinfo文件中计算出的与rsa相关的特征显示在摘要查看器中。gydF4y2Ba1gydF4y2Ba(b))。gydF4y2Ba
概述RSAtrace3DgydF4y2Ba
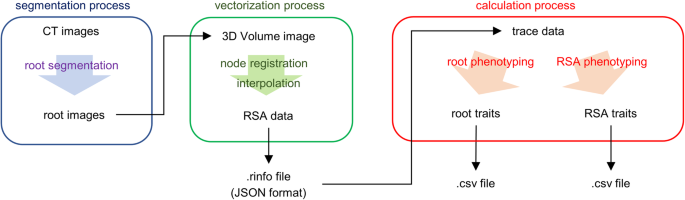
RSAtrace3D的过程和数据流如图所示。gydF4y2Ba2gydF4y2Ba,分为三个过程:分割、向量化和计算过程。在分割过程中,从原始CT图像中分离出根段。此功能不由RSAtrace3D处理,应使用根分割软件执行,如RSAvis3D [gydF4y2Ba20.gydF4y2Ba].在向量化过程中,根段通过应用GUI操作向量化。操作符注册基点(节点),例如根段的两端,通过节点之间的插值向量化。向量化在单个根上执行。此外,向量化数据存储为rinfo文件。在计算过程中,使用向量化数据计算单个根和rsa相关的特征,并将它们导出为CSV(逗号分隔值)文件。gydF4y2Ba
分割过程gydF4y2Ba
体积数据应为8位灰度图像并存储在单个目录中,以3D NumPy数组的形式导入[gydF4y2Ba32gydF4y2Ba].建议对根片段增强的体积数据使用根向量化软件,如RSAvis3D [gydF4y2Ba20.gydF4y2Ba].gydF4y2Ba
向量化的过程gydF4y2Ba
RSA数据格式gydF4y2Ba
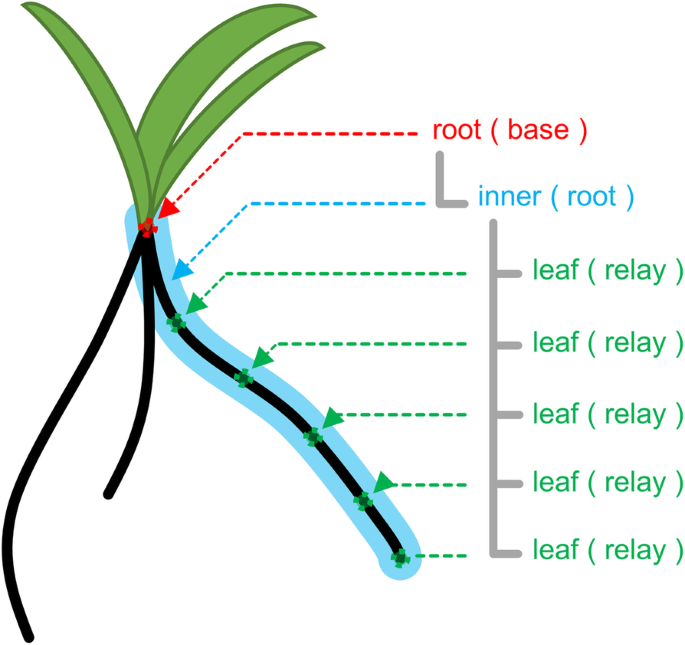
RSA向量化数据使用树形结构对象进行管理。gydF4y2Ba3.gydF4y2Ba).在本例中,树的深度为2。根系在土壤中的位置用欧氏坐标表示。根节点(深度为0)包含所有组成RSA的单根的信息。根节点包含播种种子的位置坐标。内部节点(深度1)包含单个与根相关的信息,包括几个叶节点(深度2),其中包含指示根片段位置的坐标。例如,具有1个根和2个冠根的RSA用包含3个内节点的1个根节点表示。在本研究中,根节点、内节点和叶节点从此分别被写成基节点、根节点和中继节点。gydF4y2Ba
节点间的作线和插补gydF4y2Ba
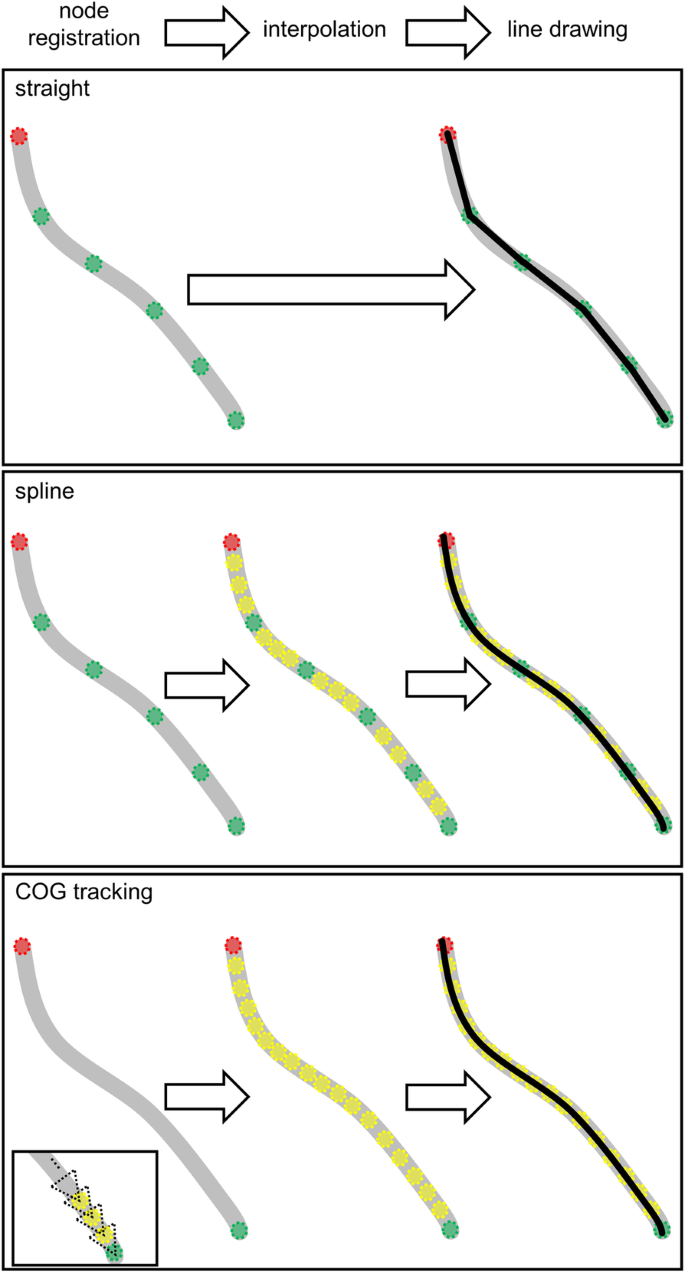
RSAtrace3D根据基节点和中继节点的坐标向量化单根,制作连线节点来表示单根形状。有三种选择可以制作直线:“直线”、“样条”和“COG跟踪”(图4)。gydF4y2Ba4gydF4y2Ba).“直”将相邻节点连接成直线折线。为了表示一个根的复杂曲线,需要注册多个中继节点。通过在SciPy的“interpolate”模块中使用函数“splprep”自动添加节点(插值节点),“样条曲线”通过所有基本节点和中继节点生成一条样条曲线[gydF4y2Ba33gydF4y2Ba].它给出了一条平滑的直线,但曲线形状被迫是样条曲线。“COG跟踪”通过自动跟踪从距离基本节点最远的节点到通过剩余节点的基本节点的单个根来绘制曲线。在移动方向上每4个体素利用根段的COG进行校正,并添加插值节点。此外,“COG跟踪”也给出了一条平滑的直线,很可能适合原始的根曲线。该插值过程(算法)可根据用户需求进行定制和扩展。gydF4y2Ba
计算过程gydF4y2Ba
单根和rsa相关的特征计算过程gydF4y2Ba
单根相关性状:单根相关性状利用节点和体积信息进行测度。RSAtrace3D生成来自节点的向量化根数据。因此,计算根的形状和尺寸测量是快速和容易的。例如,本研究计算了根的生长角(水平线与连接两端节点的线的夹角)和长度。根生长角是应用三角函数计算的角度,根长是相邻节点之间的累积距离。考虑到gydF4y2BangydF4y2Ba的单根和欧氏坐标的插值节点数gydF4y2Ba我gydF4y2Ba-th节点表示为gydF4y2BaPgydF4y2Ba我gydF4y2Ba(gydF4y2BaxgydF4y2Ba我gydF4y2Ba,gydF4y2BaygydF4y2Ba我gydF4y2Ba,gydF4y2BazgydF4y2Ba我gydF4y2Ba),为根生长角gydF4y2BaθgydF4y2Ba(弧度)由下式计算:gydF4y2Ba
假设体素分辨率表示为gydF4y2BargydF4y2Ba(毫米/体素)、根长度gydF4y2BalgydF4y2Ba(cm)的计算公式如下:gydF4y2Ba
rsa相关特征:鉴于此gydF4y2BaNgydF4y2Ba表示单根和的个数gydF4y2Ba我gydF4y2Ba-th根生长角表示为gydF4y2BaθgydF4y2Ba我gydF4y2Ba,平均根生长角度gydF4y2Ba\(\眉题θ}{\ \)gydF4y2Ba由下式计算:gydF4y2Ba
考虑到gydF4y2Ba我gydF4y2Ba-th根长度表示为gydF4y2BalgydF4y2Ba我gydF4y2Ba,总根长度gydF4y2BaTLgydF4y2Ba(cm)由下式计算:gydF4y2Ba
根系分布指数(RDI)是一个表示植物根系增殖深度的参数[gydF4y2Ba34gydF4y2Ba,gydF4y2Ba35gydF4y2Ba,gydF4y2Ba36gydF4y2Ba].它是根系垂直分布的质心,通过测量根系在土壤中的长度,并将它们的深度平均值与深度[gydF4y2Ba34gydF4y2Ba,gydF4y2Ba35gydF4y2Ba].在RDI计算之前,节点之间以体素分辨率插值。已知插值节点的个数gydF4y2Ba我gydF4y2Bath根gydF4y2Ba\(\打翻{\急性{\ mkern6mu}} {n_I} \)gydF4y2Ba的欧氏垂直线坐标gydF4y2Ba我gydF4y2Bath节点gydF4y2Ba我gydF4y2Ba-th根表示为gydF4y2BazgydF4y2Ba(gydF4y2Ba我gydF4y2Ba,gydF4y2Ba我gydF4y2Ba)gydF4y2Ba,基节点的欧氏纵坐标表示为gydF4y2BazgydF4y2BabgydF4y2Ba, RDI (cm)由下式计算:gydF4y2Ba
结果与讨论gydF4y2Ba
根向量化gydF4y2Ba
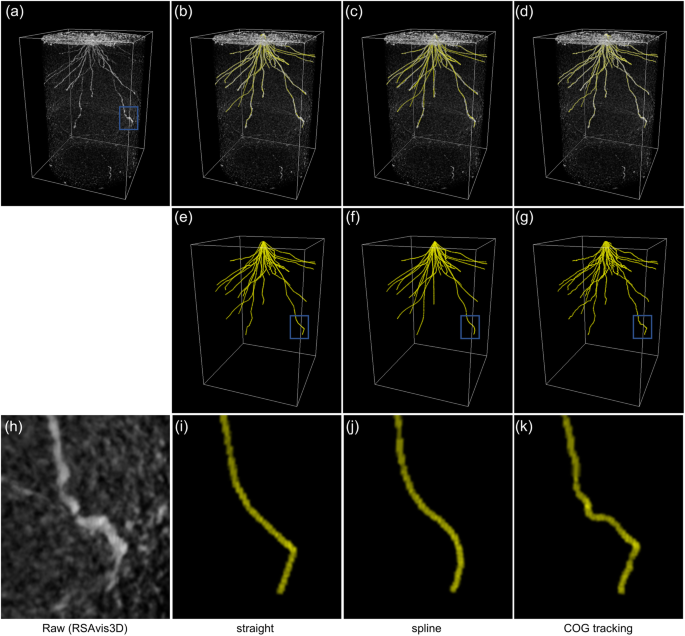
水稻品种Kinandang Patong (KP, ssp)的胚根和冠根。热带gydF4y2Ba粳稻gydF4y2Ba),使用RSAtrace3D向量化。强化播后26天的根段(26- das) KP [gydF4y2Ba20.gydF4y2Ba,使用RSAvis3D处理的x射线CT图像。KP的CT三维渲染图像,以白色着色,如图所示。gydF4y2Ba5gydF4y2Ba(a),以及用“直线”、“样条”和“COG跟踪”合并的矢量折线(黄色),如图所示。gydF4y2Ba5gydF4y2Ba(b) - (d)。当画的线在原来的根内部时,它被涂成白色。此外,三种方法的根系总体分布相似(图5)。gydF4y2Ba5gydF4y2Ba(e) - (g)),但在细节上观察到差异(图5)。gydF4y2Ba5gydF4y2Ba(h) - (k))。与“直线”和“样条”的折线相比(图5)。gydF4y2Ba1gydF4y2Ba(i)和(j)),经过“COG跟踪”的折线紧密地跟踪了原始根段(图5)。gydF4y2Ba5gydF4y2Ba(h)和(k))。通过“直线”、“样条”和“COG跟踪”向量化所需的点击数和时间见表gydF4y2Ba1gydF4y2Ba.“COG跟踪”需要10分钟的样本,但需要超过50%的点击和时间比“直线”或“样条”是最不费力的方法。总的来说,与“直线”和“样条”相比,“COG跟踪”是最精确、最省力的方法。gydF4y2Ba
三种向量化方法的跟踪性能比较。CT图像采用RSAvis3D处理,RSAtrace3D向量化。(gydF4y2Ba一个gydF4y2Ba) x射线CT图像中26-DAS KP的s根三维绘制。x射线CT图像(gydF4y2Ba一个gydF4y2Ba)与向矢量折线合并(gydF4y2BabgydF4y2Ba)“直”,(gydF4y2BacgydF4y2Ba)“样条”,和(gydF4y2BadgydF4y2Ba)“齿轮跟踪。”向量化的折线用黄色表示。向量化折线(gydF4y2BaegydF4y2Ba), (gydF4y2BafgydF4y2Ba)和(gydF4y2BaggydF4y2Ba)与(gydF4y2BabgydF4y2Ba), (gydF4y2BacgydF4y2Ba)和(gydF4y2BadgydF4y2Ba),分别。被蓝色方框圈出的内部放大版(gydF4y2Ba一个gydF4y2Ba), (gydF4y2BaegydF4y2Ba), (gydF4y2BafgydF4y2Ba)和(gydF4y2BaggydF4y2Ba)载于(gydF4y2BahgydF4y2Ba), (gydF4y2Ba我gydF4y2Ba), (gydF4y2BajgydF4y2Ba)和(gydF4y2BakgydF4y2Ba),分别。矩形表示(宽)180毫米×(深)180毫米×(高)258毫米gydF4y2Ba
测量应用gydF4y2Ba
为了评估测量精度,我们比较了手工测量和RSAtrace3D三种功能的根系生长角度和长度。使用了以下三个水稻品系:IR64 (ssp。gydF4y2Ba籼稻gydF4y2Ba), Dro1-NIL (ssp。gydF4y2Ba籼稻gydF4y2Ba), KP。此外,IR64的根浅,而KP的根深。Dro1-NIL具有介于IR64和KP之间的中间生根角。此外,它是IR64引入KP等位基因的近等基因系gydF4y2Ba更深层次的加油1gydF4y2Ba(gydF4y2BaDRO1gydF4y2Ba)基因,该基因从IR64和KP之间的双亲本群体中分离出来,对KP的深生根特性有贡献。有线篮法[gydF4y2Ba20.gydF4y2Ba]用于土壤基质中的根系取样。在除去土壤时,保留RSA的三维结构的有线篮子被埋在了花盆里。IR64、Dro1-NIL和KP种子分别在有线篮子内的土壤基质煅烧粘土中播种。4周后,用x射线CT扫描花盆,从花盆中挖出钢丝篮。应用RSAvis3D对x射线CT图像进行处理,利用RSAtrace3D导入得到的根系图像,对胚根和冠根进行矢量化。通过人工测量,根据根系从篮网发出的位置测量根系生长角。此外,收集篮内的根系,并使用扫描仪(Expression 12000XL,精工爱普生公司,Suwa, Nagano, Japan)进行扫描,并使用SmartRoot测量根系长度[gydF4y2Ba23gydF4y2Ba].gydF4y2Ba
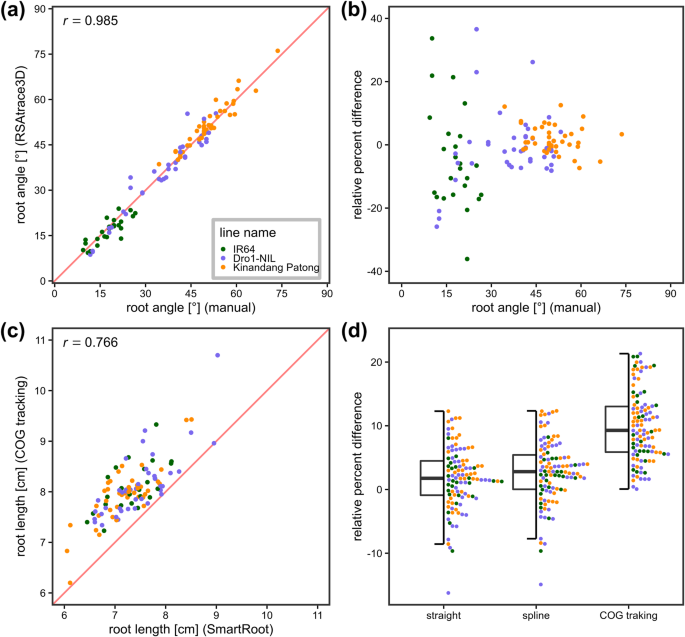
对比了手动测量和RSAtrace3D测量结果。gydF4y2Ba6gydF4y2Ba).在根的生长角度上,观察到所有三条线的高度正相关(图。gydF4y2Ba6gydF4y2Ba(一),gydF4y2BaRgydF4y2Ba= 0.985)。手动测量和RSAtrace3D测量之间的相对百分比差(RPD)的方差在浅角区域变大(图1)。gydF4y2Ba6gydF4y2Ba(b))。这是因为单位误差的影响随着角度的减小而增加。在从多个根测量平均根生长角的情况下,由于RPD在x轴上是对称的,因此RPD的高方差影响很小。在根长方面,3个株系均呈正相关(gydF4y2BaRgydF4y2Ba= 0.766),并且,与手动测量相比,RSAtrace3D测量在所有情况下都是高的(图。gydF4y2Ba6gydF4y2Ba(c))。我们计算了在使用“直线”、“样条”和“COG跟踪”方法的情况下,RSAtrace3D相对于SmartRoot的RPD。gydF4y2Ba6gydF4y2Ba(d))。“直线”和“样条”的RPD中位数约为0%,“COG跟踪”的RPD中位数约为10%。因此,这种差异来自于利用RSAtrace3D对三维波形根的精确跟踪。gydF4y2Ba5gydF4y2Ba(h) - (k))。此外,“直”和“样条”会低估根长。用3D波形根进行二维扫描同样会低估根的长度。gydF4y2Ba6gydF4y2Ba(c)和(d))。总的来说,RSAtrace3D中的“COG跟踪”是测量三维波形根最可靠的方法。gydF4y2Ba
手动和RSAtrace3D方法的测量比较。(gydF4y2Ba一个gydF4y2Ba)每个根的根生长角(两端节点之间的角度)的散点图。标识线显示为红色。皮尔逊的相关系数显示。(gydF4y2Bab)gydF4y2Ba根系生长角度的rpd (RSAtrace3D中的“COG跟踪”测量与手动测量相比)。(gydF4y2BacgydF4y2Ba)每个根的根长散点图。标识线显示为红色。皮尔逊的相关系数显示。(gydF4y2BadgydF4y2Ba根长度的rpd (RSAtrace3D中的“COG跟踪”测量相对于手动测量)。比较了“直线”、“样条”和“COG跟踪”三种方法。对于箱形图,其顶部和底部分别标记第一和第三个四分位数。此外,中心线表示中位数,而须表示距铰链1.5倍的四分位范围内的观测值的范围gydF4y2Ba
以不同生根类型的3个水稻品系为例gydF4y2Ba
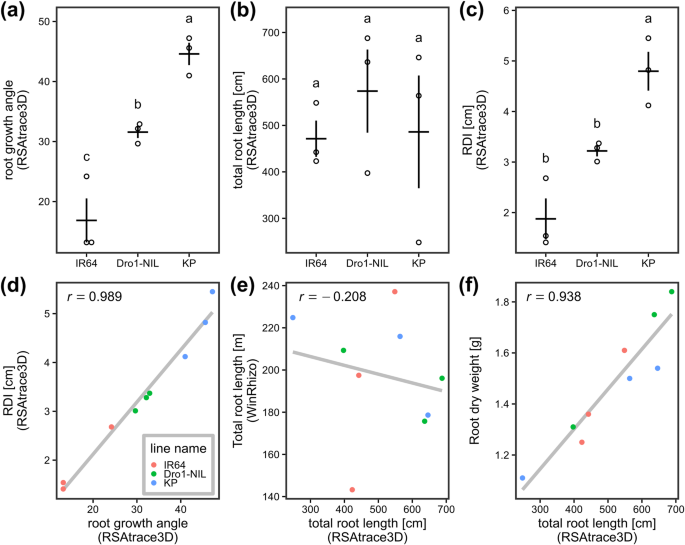
利用RSAtrace3D对IR64、Dro1-NIL和KP的根参数进行定量评估。IR64、Dro1-NIL和KP各培养3个,培养2个月后进行x射线CT扫描。CT图像采用RSAvis3D处理,RSAtrace3D向量化。CT扫描后,收集土壤中的根系,使用WinRHIZO™Pro 2017a软件(Regent Instruments, Canada)测量根系总长度。将扫描根放入烤炉中烘干,测量根系干重(RDW)。具有代表性的RSA图像如图所示。gydF4y2Ba7gydF4y2Ba.如前所述,观察到不同的根分布特性。利用RSAtrace3D软件自动计算3个水稻品系的根系生长角度、根系总长度和RDI(图1)。gydF4y2Ba8gydF4y2Ba(一)- (c))。3条线的根系生长角度不同。gydF4y2Ba8gydF4y2Ba(a)),而三条线的根长相似(图1)。gydF4y2Ba8gydF4y2Ba(b))。此外,三条线的RDIs也不同(图。gydF4y2Ba8gydF4y2Ba(c))。根系生长角与RDI高度相关(图1)。gydF4y2Ba8gydF4y2Ba(d)),表明RDI依赖于根系生长角度。利用RSAtrace3D测量的总根长与WinRHIZO测量的结果不相关(图2)。gydF4y2Ba8gydF4y2Ba(e))。在本研究中,为了从RSA形状相关数据中排除根系接触墙体,我们使用RSAvis3D在直径为20 cm的花盆中仅可视化了一个直径为18 cm的圆柱形区域。此外,RSAtrace3D处理的总根长与RDW高度相关(图1)。gydF4y2Ba8gydF4y2Ba(f))。认为RSAvis3D未显示根界的贡献较小,其中细根占总根干重的比重较大。gydF4y2Ba
RSAtrace3D测量方法及其与传统方法的比较。(gydF4y2Ba一个gydF4y2Ba根生长角(两端节点之间的夹角),gydF4y2BabgydF4y2Ba)总根长,及(gydF4y2BacgydF4y2Ba) IR64的RDI, Dro1-NIL,和KP。横线和垂线分别表示标准误差的均值和范围(样本量= 3)。每个字母都表明统计学上的显著差异(图基-克雷默测验,gydF4y2BaαgydF4y2Ba= 0.05)。的比较(gydF4y2BadgydF4y2Ba)根生长角与RDI的比值,(gydF4y2BaegydF4y2Ba)使用RSAtrace3D的根长度与使用WinRhizo的根长度比较,以及(gydF4y2BafgydF4y2Ba)使用RSAtrace3D和RDW的总根长度。这些线表示线性回归线。皮尔逊的相关系数显示gydF4y2Ba
结论gydF4y2Ba
RSAtrace3D是一款用于单性状3D RSA表型分析的RSA向量化软件。通过引入基于cog的跟踪算法,我们观察到矢量化过程比简单地使用直线连接节点快4倍。根据根系样本量的不同,水稻RSA向量化所需时间约为10分钟。例如,RSAvis3D可视化水稻RSA 15分钟[gydF4y2Ba20.gydF4y2Ba],包括扫描和重建时间。在这种情况下,可以在等待扫描完成的同时对上一次CT扫描的RSA进行向量化。当处理大量的根样本时,这种使用RSAvis3D和RSAtrace3D的高通量图像分析管道是有用的。一旦转换为矢量,就需要非常少量的数据来表示根系统。在案例研究中,我们使用了三种稻种中的三种作为研究对象。因此,样本数量为9个,其总数据大小在x射线CT图像(16位标记图像文件格式(TIFF))中约为16 GB,在RSAvis3D图像(8位便携式网络图形(PNG))中约为800 Mb,在RSAtrace3D矢量数据中约为500 Kb。这种小的数据量使得在研究人员之间共享数据变得容易,从而促进了再分析,从而加速了根研究。由于RSA向量化和表型分型算法具有较高的可扩展性,RSAtrace3D不仅可以应用于X-ray CT图像中的水稻,还可以应用于各种3D图像中的其他单性状。RSAtrace3D程序可从[gydF4y2Ba37gydF4y2Ba].gydF4y2Ba
可用性和需求gydF4y2Ba
项目名称:ROOTomics。gydF4y2Ba
项目主页:gydF4y2Bahttps://rootomics.dna.affrc.go.jp/en/gydF4y2Ba
操作系统:跨平台。gydF4y2Ba
编程语言:Python3。gydF4y2Ba
其他要求:Python 3.6或更高版本。gydF4y2Ba
许可协议:麻省理工学院许可证。gydF4y2Ba
非学术人员使用的任何限制:需要商业许可证。gydF4y2Ba
数据和材料的可用性gydF4y2Ba
本研究中所用图形的植物材料和原始数据均可根据合理要求从通讯作者处获得。gydF4y2Ba
缩写gydF4y2Ba
- RSA:gydF4y2Ba
-
根系统架构gydF4y2Ba
- CT:gydF4y2Ba
-
计算机断层扫描gydF4y2Ba
- 核磁共振成像:gydF4y2Ba
-
磁共振成像gydF4y2Ba
- 齿轮:gydF4y2Ba
-
重心gydF4y2Ba
- RDI:gydF4y2Ba
-
根分布指数gydF4y2Ba
- KP:gydF4y2Ba
-
Kinandang巴东gydF4y2Ba
- DAS:gydF4y2Ba
-
几天后播种gydF4y2Ba
- DRO1gydF4y2Ba:gydF4y2Ba
-
更深层次的加油1gydF4y2Ba
- RPD:gydF4y2Ba
-
相对百分比差异gydF4y2Ba
- RDW:gydF4y2Ba
-
根干重gydF4y2Ba
- GB:gydF4y2Ba
-
ggydF4y2Ba
参考文献gydF4y2Ba
- 1.gydF4y2Ba
根构型与植物生产力。植物杂志。1995;109:7-13。gydF4y2Ba
- 2.gydF4y2Ba
根系结构:来自拟南芥和谷类作物的见解。Philos Trans Royal Soc B: Biol science . 2012; 367:1441-52。gydF4y2Ba
- 3.gydF4y2Ba
与养分吸收有关的根系结构。阿阿格龙。1970;22:159 - 201。gydF4y2Ba
- 4.gydF4y2Ba
根系分布与水分吸收和有效性的关系。阿格龙j . 1964; 56:41-5。gydF4y2Ba
- 5.gydF4y2Ba
德·多洛多特,福斯特,Pagès L, Price A, Tuberosa R, Draye X.根系结构:作物遗传改良的机遇与制约。植物学报2007;12:474-81。gydF4y2Ba
- 6.gydF4y2Ba
Gowariker V, Krishnamurthy VN, Gowariker S, Dhanorkar M, Paranjape K.肥料百科。新泽西州霍博肯:John Wiley & Sons, Inc;2009.gydF4y2Ba
- 7.gydF4y2Ba
在缺水环境下提高作物产量的性状评价。阿阿格龙。1990;43:107-53。gydF4y2Ba
- 8.gydF4y2Ba
高达,王晓燕,王晓燕。水稻根系生物学与抗旱性的遗传改良。《田间作物》2011;122:1-13。gydF4y2Ba
- 9.gydF4y2Ba
Böhm W.研究根系的方法,卷33。柏林:施普林格科学与商业媒体;1979.gydF4y2Ba
- 10.gydF4y2Ba
朱杰,Ingram PA, Benfey PN, Elich T.从实验室到田间,根系结构表型的新方法。植物生物学杂志,2011;14:310-7。gydF4y2Ba
- 11.gydF4y2Ba
吉野佳,田中田,田中田,等。在根系中采用更深层次的综合多组学方法来开发适应气候变化的水稻。摩尔品种。2019;39:165。gydF4y2Ba
- 12.gydF4y2Ba
Heeraman DA, Hopmans JW, Clausnitzer V.植物原位根系的三维x射线计算机断层成像。土壤植物。1997;189:167 - 79。gydF4y2Ba
- 13.gydF4y2Ba
张晓燕,张晓燕,张晓燕,等。植物根系的核磁共振成像分析。在:计算机视觉,成像和计算机图形学理论与应用。施普林格;2013.411 - 25页。gydF4y2Ba
- 14.gydF4y2Ba
Clark RT, MacCurdy RB, Jung JK, Shaff JE, McCouch SR, Aneshansley DJ,等。三维根表型与一个新的成像和软件平台。植物杂志。2011;156:455 - 65。gydF4y2Ba
- 15.gydF4y2Ba
梅茨纳R, Eggert A, van Dusschoten D, Pflugfelder D, Gerth S, Schurr U,等。土壤根系三维成像的MRI和x射线CT技术的直接比较:根系性状量化的潜力和挑战。工厂方法。2015;十一17。gydF4y2Ba
- 16.gydF4y2Ba
Mairhofer S, Zappala S, Tracy SR, Sturrock C, Bennett M, Mooney SJ,等。RooTrak:利用视觉跟踪从x射线显微计算机断层扫描图像自动恢复土壤中的三维植物根系结构。植物杂志。2012;158:561-9。gydF4y2Ba
- 17.gydF4y2Ba
Mairhofer S, Zappala S, Tracy S, Sturrock C, Bennett MJ, Mooney SJ,等。通过x射线μ计算机断层扫描从土壤中恢复完整的植物根系结构。工厂方法。2013;九8。gydF4y2Ba
- 18.gydF4y2Ba
Tracy SR, Black CR, Roberts JA, McNeill A, Davidson R, Tester M,等。量化土壤压实对三个小麦品种(gydF4y2Ba小麦gydF4y2BaL.)使用x射线微型计算机断层扫描(CT)。土壤植物。2012;353:195 - 208。gydF4y2Ba
- 19.gydF4y2Ba
高伟,Schlüter S, Blaser SR,沈杰,Vetterlein D.一种基于形状的x射线ct图像土壤根系自动快速分割方法。土壤植物。2019;441:643-55。gydF4y2Ba
- 20.gydF4y2Ba
Teramoto S, Takayasu S, Kitomi Y, Arai-Sanoh Y, Tanabata T, Uga Y.利用x射线计算机断层扫描水稻根系结构的高通量三维可视化。工厂方法。2020;16:66。gydF4y2Ba
- 21.gydF4y2Ba
范杜舒腾D,梅茨纳R,科赫斯J, Postma JA, Pflugfelder D, Bühler J,等。利用磁共振成像技术对土壤中生长的植物根系进行定量三维分析。植物杂志。2016;170:1176 - 88。gydF4y2Ba
- 22.gydF4y2Ba
高伟,Blaser SR, Schlüter S,沈杰,Vetterlein D.局部施磷对玉米根系生长和土壤养分动态的影响(gydF4y2Ba玉米gydF4y2Ba)及蚕豆(gydF4y2Ba蚕豆根尖gydF4y2Ba)在苗期。土壤植物。2019;441:469 - 83。gydF4y2Ba
- 23.gydF4y2Ba
Lobet G, Pagès L, Draye X.一个新的图像分析工具箱,使根系结构定量分析。植物杂志。2011;157:29-39。gydF4y2Ba
- 24.gydF4y2Ba
皮埃雷特,柯比M,莫兰C.薄平板系统中植物根系生长和水分吸收的同步x射线成像。在:根:植物和地球之间的动态界面。施普林格;2003: 361 - 373。gydF4y2Ba
- 25.gydF4y2Ba
Dhondt S, Vanhaeren H, Van Loo D, Cnudde V, Inzé D.高分辨率x射线计算机断层扫描植物结构可视化。植物学报2010;15:419-22gydF4y2Ba
- 26.gydF4y2Ba
Mooney SJ, Pridmore TP, Helliwell J, Bennett MJ。发展x射线计算机断层扫描技术,以无创成像三维土壤根系结构。土壤植物。2012;352:1-22。gydF4y2Ba
- 27.gydF4y2Ba
Plenge E, Poot DH, Bernsen M, Kotek G, Houston G, Wielopolski P,等。MRI中的超分辨率方法:它们能改善分辨率、信噪比和采集时间之间的权衡吗?Magn Reson Med. 2012; 68:1983-93。gydF4y2Ba
- 28.gydF4y2Ba
Adams C, Jacobson A, Bugbee B.陶瓷聚合体吸附和解吸化学:作为无土介质组成部分的意义。植物营养学报,2014;37:1345-57。gydF4y2Ba
- 29.gydF4y2Ba
Kuka K, Illerhaus B, Fritsch G, Joschko M, Rogasik H, Paschen M, Schulz H, Seyfarth M.一种提取x射线计算机断层扫描未受干扰土壤样品的新方法。非dest Test. 2013:(8)。gydF4y2Ba
- 30.gydF4y2Ba
Python。gydF4y2Bahttps://www.python.org/gydF4y2Ba已于2020年10月30日访问。gydF4y2Ba
- 31.gydF4y2Ba
Json格式。gydF4y2Bahttps://www.json.org/json-en.htmlgydF4y2Ba已于2020年10月30日访问。gydF4y2Ba
- 32.gydF4y2Ba
Walt Svd, Colbert SC, Varoquaux G. NumPy数组:一种高效数值计算的结构。计算机科学与工程。2011;13:22-30。gydF4y2Ba
- 33.gydF4y2Ba
Jones E, Oliphant T, Peterson P. SciPy: Python的开源科学工具gydF4y2Bahttps://www.scipy.orggydF4y2Ba.已于2020年10月30日访问。gydF4y2Ba
- 34.gydF4y2Ba
王晓燕,王晓燕,王晓燕。小麦品种根系生长角度与田间根系垂直分布的关系。作物学报1993;62:565-70。gydF4y2Ba
- 35.gydF4y2Ba
小麦根系的重向性响应、生长角和垂直分布(gydF4y2Ba小麦gydF4y2Bal .)。土壤植物。1994;165:323-6。gydF4y2Ba
- 36.gydF4y2Ba
泉Y,内田K,饭岛M.免耕小麦-大豆轮作作物产量与根系发育的关系。植物科学2004;7:329-36。gydF4y2Ba
- 37.gydF4y2Ba
ROOTomics。gydF4y2Bahttps://rootomics.dna.affrc.go.jp/en/gydF4y2Ba已于2020年10月30日访问。gydF4y2Ba
致谢gydF4y2Ba
我们感谢福田洋子和高桥雅子的实验助手。我们感谢测试人员Yoko Fukuda, Saki Yoshida和Yuko Numajiri。gydF4y2Ba
资金gydF4y2Ba
本研究得到了日本JST CREST Grant Number JPMJCR17O1的支持。gydF4y2Ba
作者信息gydF4y2Ba
从属关系gydF4y2Ba
贡献gydF4y2Ba
ST设计了研究,获取了图像数据,构建和评估了软件,并撰写了稿件。TT修改了手稿。YU协调了项目,设计了研究,修改了手稿。所有作者均已阅读并认可该手稿。gydF4y2Ba
相应的作者gydF4y2Ba
道德声明gydF4y2Ba
伦理批准和同意参与gydF4y2Ba
不适用。gydF4y2Ba
同意出版gydF4y2Ba
不适用。gydF4y2Ba
相互竞争的利益gydF4y2Ba
作者声明他们没有利益冲突。gydF4y2Ba
额外的信息gydF4y2Ba
出版商的注意gydF4y2Ba
施普林格自然对出版的地图和机构附属的管辖权要求保持中立。gydF4y2Ba
权利和权限gydF4y2Ba
开放获取gydF4y2Ba本文遵循创作共用署名4.0国际许可协议(Creative Commons Attribution 4.0 International License),该协议允许在任何媒体或格式中使用、分享、改编、分发和复制,只要您给予原作者和来源适当的署名,提供创作共用许可协议的链接,并说明是否有更改。本文中的图片或其他第三方材料包含在文章的创作共用许可中,除非在材料的信用额度中另有说明。如果材料不包含在文章的创作共用许可中,并且您的预期用途不被法律法规允许或超出了允许的用途,您将需要直接从版权所有者那里获得许可。欲查看此许可证的副本,请访问gydF4y2Bahttp://creativecommons.org/licenses/by/4.0/gydF4y2Ba.创作共用公共领域奉献放弃书(gydF4y2Bahttp://creativecommons.org/publicdomain/zero/1.0/gydF4y2Ba)适用于本文提供的数据,除非在数据的信用额度中另有说明。gydF4y2Ba
关于这篇文章gydF4y2Ba
引用这篇文章gydF4y2Ba
Teramoto, S., Tanabata, T. & Uga, Y. RSAtrace3D:用于测量单子叶植物根系结构的稳健向量化软件。gydF4y2BaBMC植物杂志gydF4y2Ba21日,gydF4y2Ba398(2021)。https://doi.org/10.1186/s12870-021-03161-9gydF4y2Ba
收到了gydF4y2Ba:gydF4y2Ba
接受gydF4y2Ba:gydF4y2Ba
发表gydF4y2Ba:gydF4y2Ba
DOIgydF4y2Ba:gydF4y2Bahttps://doi.org/10.1186/s12870-021-03161-9gydF4y2Ba
关键字gydF4y2Ba
- 图像分析gydF4y2Ba
- 3 d体积gydF4y2Ba
- 三维分析gydF4y2Ba
- PythongydF4y2Ba
- 根的长度gydF4y2Ba
- 根系生长角度gydF4y2Ba
- 根的分布gydF4y2Ba