抽象的
背景
冰藻衣原体sp. ice - l是南极海冰生态系统初级生产力的主要贡献者,并能很好地适应极端恶劣的环境。然而,其适应机制衣原体sp. ICE-L与海冰环境的关系尚不清楚。研究大学生的适应策略衣原体sp。冰-1,我们研究了叶绿体光合基因的分子演变,这些基因对于南极海冰的碳水化合物和能量的积累至关重要。
结果
60个叶绿体蛋白质编码基因衣原体分支位点试验检测到阳性选择的显著特征atpB那psaB,rbcl.基因衣原体与光合机制有关的。这些正向选择的基因被进一步确认为在趋同进化中衣原体sp. ICE-L与耐盐藻类Dunaliella Salina..
结论
我们的研究提供了表现出的证据表明镜头组分衣原体sp. ICE-L在极端环境下表现出适应性进化。南极冰藻适应极端环境的叶绿体蛋白编码基因遵循功能特异性和谱系特异性的模式,受到正向达尔文选择的作用。此外,三个正向选择的基因与收敛取代衣原体sp。鉴定冰-1,这些基因的适应性修饰在功能上的蛋白质的重要区域中。我们的研究为未来对绿藻光合作用生物化学和生理影响的未来实验提供了基础。
背景
南极区域是特别恶劣的环境,温度极低。从冬季到夏季(从-80°C至5°C),高UV-B辐射和交替的阳光和黑暗的季节性波动是有机体在南极洲生存的主要挑战[1].南极海冰是极地极端环境的重要组成部分,它在低温、高盐度和低光条件下构成了一个浓缩盐水通道系统[2].在这种恶劣的环境中生存需要生理和新陈代谢方面的复杂适应。南极冰藻在海冰中生长旺盛,它们的大量生长使它们成为海冰生态系统初级生产力的主要贡献者[2那3.].据报道,南极冰藻形成一系列生理和生物化学机制,以适应极端环境[1那4.那5.那6.那7.].快速增长的分子数据为我们研究适应机制提供了新的途径。在分子水平上揭示适应策略可以揭示藻类的进化模式,并为藻类对极端环境的适应性提供新的见解。
绿藻通过叶绿体的光合作用将无机碳转化为有机化合物,光合系统对非生物环境胁迫(弱光、低温和高盐度)非常敏感。叶绿体是光合作用的反应中心,叶绿体基因组是光合作用进化研究的有用资源[8.那9.].这种母性遗传的非重组叶绿体基因组编码光合系统的许多重要亚单位(有些亚单位是由核基因编码的),不同绿藻的叶绿体基因组大小不同[10.那11.].三种模式生物的比较基因组分析(拟南芥那衣藻reinhardtii和Thermosynechococcus elongatus.)表明48个叶绿体基因可分为两大类:29个光合器官基因;叶绿体遗传系统组成的19个基因。这29个叶绿体基因编码5个光合复合体:光系统I (PSI),光系统II (PSII),细胞色素B.6.F(CytB.6.F),ATP合成和Rubisco。蛋白质复合物Psi,psii和细胞色素B.6.F(CytB.6.F)是膜固有的。这些配合物形成光合电子传输链,其可以将电子从PSII转移到NADP的氧化PSI反应中心+减少到NADPH。PSI和PSII都是应力敏感性,编码两种复合物的基因可以在转录和转录后水平进行反应对非生物胁迫[12.那13.].在电子转移过程中,质子梯度被叶绿体ATP合酶构建和利用。产生的ATP可用于CO的光合固定过程2.Rubisco是外部的膜,催化二氧化碳同化的还原戊糖磷酸途径的第一步。高浓度的NaCl和低温可能限制Rubisco的活性,这会抑制CO的固定2[14.那15.].的rbcl.在适应极端环境的许多植物中编码Rubisco的基因显示了影响非生物应激反应的Rubisco中的各种氨基酸取代[14.].
南极植物在光合体系的五种复合物中发展了许多适应性分子机制,以在恶劣环境中存活[16.那17.那18.].据报道Colobanthus quitensis.(被子植物)生活在南极洲已经适应了保持更快的光合系统修复速度[19.].南极的大型藻类(如Himantothallus grandifolius和Desmarestia anceps)进化出高光合效率、低光需求的光合作用和显著的抗紫外线能力[20.].有趣的是,南极冰上有硅藻Amphiprora kufferathii利用附生细菌消耗光合作用产生的活性氧[21.].南极植物的越来越多的分子数据将有助于从进化角度调查光合作用对南极洲极端环境的调整。据报道,积极选择和迅速发展的动物中的基因促成了极端环境适应[22.那23.那24.].在植物中,苔藓Rubisco基因(参与碳固定)的正选择证据与它对大气CO水平下降的适应有关2自从他们在奥莫瓦主义者的起源以来[25.].内石器时代绿藻中与光合作用机制有关的基因Ostreobium Queketti由于其低轻型生活方式而显示出强烈的净化选择[26.].耐盐剂的基因组分析胡杨展示编码光合电子传输链的基因的快速进化[27.].
绿色藻类衣原体sp。冰-L从浮海冰中分离,最佳生长温度范围为4-10°C。作为南极海冰的主要生产力,衣原体sp. ICE-L进化出特定的形态特征,以适应极端环境,如色素、脂类和脂肪酸含量的变化,以维持类囊体膜的稳定和叶绿体正常的生理功能[7.].南极洲的特别恶劣的环境可能会在光合基因中留下足迹衣原体sp。通过改变分子进化率的冰-1。然而,几乎没有关于适应对该藻类光合作用的极端环境的基因证据。
还有其他绿藻可能适应相似的环境压力。Coccomyxa subellipsoideaC-169是一个小型细长的非运动单细胞绿色藻类,在大理石点,在1959/60年的极地夏天分离,在大理石点,其中有大潮湿的区域覆盖着厚厚的晶沉nostoc公社[28.的主要环境因素Coccomyxa subellipsoideaC-169是低光和低温。小球藻sp. ArM0029B从北极地区的浮冰中分离出来[29.],低温被认为是主要的环境压力。Dunaliella Salina.是在极端盐水环境中蓬勃发展的卤化藻[30.],高盐度则为非生物胁迫Dunaliella Salina..这些绿藻以及衣原体sp。生活在极端环境中的ICE-L是相对调查不同非生物胁迫的适应性策略的理想生物。
在这项研究中,我们测序了60个叶绿体蛋白质编码基因衣原体sp。冰-1,使用上述绿藻的其他可用的叶绿体基因组,生活在类似的极端环境(低光,低温和高盐度)中,研究了在光合机械中适应非生物胁迫的潜在遗传基础衣原体ICE-L sp。适应性evolutive似乎在功能(光合组分)和谱系特异性方式中靶向叶绿体的蛋白质编码组分,并且这些正选基因中的自适应修饰在功能上重要的区域。我们的分析显示了南极冰藻叶绿体蛋白编码基因的阳性选择和会聚演化的鉴定,支持对藻类中极端环境的调整与叶绿体蛋白的改变模式相关。
方法
藻类样品和DNA测序
伤害衣原体sp. ice - l是2001 - 2002年中国第18次南极科学考察期间在中国南极中山站附近的浮冰资料。的衣原体sp. ice - l从南极海冰中分离,在实验室进行单克隆培养。细胞在Provasoli海水培养基中培养[31.]在光子通量密度为40μmol光子m- 2S.- 1, 14 L: 10D循环,温度8°C。使用DNeasy Plant Mini Kit (QIAGEN Bio-Tec)提取总基因组DNA,并使用Illumina HiSeq™2000平台进行测序。
叶绿体基因的组装与注释
通过使用内部perl脚本删除适配器、poly-N和低质量读取,总共生成了6130 Mb干净读取(125-bp对端)。所有的下游分析都是基于干净的读数。我们使用SPAdes软件进行从头组装[32.]参数“--plasmID”,“--Careful”和其他默认设置。我们创建了绿藻的出版叶绿体基因组的本地数据库,并且进行了相似性搜索,以使用爆炸从叶绿体基因组中识别支架,其中截止的E值为1×10- 10.[33.].我们进一步使用了Geneious(版本9.0.4,http://www.geneious.com/)注释叶绿体基因,并使用DOGMA确认基因注释[34.]网上工具(http://dogma.ccbb.utexas.edu/).
DNA对准和系统发育推理
我们使用两个不同的程序生成多个序列对齐:肌肉[35.]和恶作剧[36.].我们使用六种叶绿素和七种Trebouxiophyceae绿藻对齐60个叶绿体蛋白编码基因(表1).核苷酸序列在密码子水平上与选项“-codon”使用肌肉和蛋白质水平,使用恶作剧选择“ - 翻译”。在对准之前从序列中取消密码子。修剪每个对齐的核苷酸序列以使用带有默认参数的GBLOCKS0.91B排除对准的位置不良位置[37.],并将其连接到单个数据集中使用亵渎。除了几个网站之外,两个对齐几乎相同。我们在随后的分析中使用了恶作剧产生的对齐数据,因为恶作剧具有较低的假阳性率[38.].的RPOB1.那RPOB2.和rpoC由于视觉评估,由于对准歧义而排除基因。
基于GTRGAMMA模型的核苷酸数据和PROTGAMMAAUTO模型的氨基酸数据,利用RAxML v8.2重建系统发生树[39.]快速启动搜索1000重复。由于高饱和度,第3密码子位置对系统发育推论有问题[40]但是,核苷酸数据只有第1和第2密码子位置用于系统发育分析,以最小化饱和度的负面影响[41.].
阳性选择下的基因鉴定
在基本模型(模型= 0,NSITE = 0的基本模型下计算了代名词(DS)和非同义替换(DN)的分支特定估计,这假设没有网站 - 方向或分支DN / DS变化)。我们丢弃了11个基因,具有高DS值,以避免DN / DS的折射率。剩余46个基因的DS值低于几乎所有分支的1,确保足够的系统发育分辨率以精确地估计整个系统发生的DN / DS [42.](附加文件1:表S1)。删除对准间隙和不确定性以避免误报[43.].密码子频率由F3×4模型确定。将剩余的46个基因分为两种功能分类(光合作用和遗传系统),并分开连接。三种不同的基于密码子的似然模型(特定于分支机构的站点和分支网站模型)用于探索选择模式并识别46个蛋白质编码基因和两个连接数据中的每一个的阳性选择。分支和分支站点模型测试需要基于先验知识分配前景分支,并且不正确的分配可能会损害测试的功率。我们研究的目标是探讨阳性选择在南极海冰藻类的适应模式中的作用,因此使用适合极端环境的四种选定的藻类来执行选择分析。
检测适应性不断的进化基因衣原体sp。ICE-L,首先使用PAML中的Codeml进行分支模型分析。分支中的非同义对同义率比ω(DN / DS)表示自然选择模式的变化,其中ω= 1,ω<1和ω> 1分别对应于中性演化,净化和正选择[44.].我们使用了三个起始ω值(0.5,1和2),以避免潜在的本地Optima。对于整个系统发育树的空模型为1Ω,而替代模型允许两个不同的Ω值衣原体sp. ICE-L和背景血统。此外,其他三种绿藻(Coccomyxa subellipsoideaC-169,小球藻sp。ArM0029B和Dunaliella Salina.)和极端生活条件下,作为前景和重复分支模型试验。用χ2分布用于确定哪个模型与阈值的零模型有统计学不同P. < 0.05. We applied the FDR correction to theP.显著性水平为0.05的多次试验的值[45.].
位点特异性模型假设,选择模式在对齐的位点之间不同,但在系统发生的分支之间没有。我们使用一对位点模型比较来检验阳性选择。替代模型允许位点特异性阳性选择,但空模型不允许(M8 vs.空M8a) [44.].LRT与χ 2比较2用相应的自由分布,并将FDR校正应用于P.以上计算的值以考虑具有0.05的显着级别的多个测试[45.].
为了检测沿着特定谱系的特定位点的阳性选择证据,改进的分支位点模型(model = 2, Nsites = 2, fixed omega = 0, omega = 2)在Codeml程序中实现[44.]与null模型(model = 2, Nsites = 2, fixed omega = 1, omega = 1)进行比较。替代模型假设四类位点:前两类位点假设在净化选择(0≤ω0. ≤ 1) or neutrality (ω1 = 1) across the phylogeny, whereas the remaining two assume sites under either purifying selection or neutrality along the background but with positive selection (ω2> 1)在前台。零模型固定了ω2前台= 1。因为分支站点模型不允许有多个前台分支,所以导致衣原体sp。冰-L,Coccomyxa subellipsoideaC-169,小球藻sp。ArM0029B和Dunaliella Salina.在每个分析中单独选择作为前景分支。用χ2分布用于确定哪个模型与阈值的零模型有统计学不同P. < 0.05. We applied the FDR correction to theP.以上计算的值以考虑具有0.05的显着级别的多个测试[45.].采用Bayes经验Bayes (BEB)方法统计识别后验概率≥0.95的正选择位点[46.].
收敛和并行进化分析
为了确定在居住地暴露于类似的环境因素的遥远谱系中是否发生了类似模式,我们进行了会聚的进化分析。收敛网站包括J. Zhang和S. Kumar所定义的“平行”和“会聚”位点[47.].我们通过PAML包中的Codeml程序重新定位了分支长度并重建了祖先氨基酸序列[44.].我们在每对物种之间识别到每对物种之间的收敛和并联氨基酸取代,其中包括以下标准的标准:(1)两者中的分别物种的氨基酸残基相同;(2)氨基酸发生在现存谱系和最近的常见祖先之间发生。然后,我们进行了泊松测试以验证观察到每个基因的收敛位点是否显着大于GCPrev-F下随机替换引起的预期数量。基因氨基酸替代模型[48.那49.].据报道,gcprevf基因模型使用少量收敛分析序列进行良好,尽管它可能导致过度收敛量的假阳性检测[49.].为了减轻可能的假阳性检测,我们使用了严格的标准,即非random趋然氨基酸取代的正面选择的基因是自适应演化的保守签名[50.那51.].我们还将FDR校正应用于P.以上计算的值以考虑具有0.05的显着级别的多个测试[45.].
自适应演化下光合基因的结构分析
为了更深入地了解非随机收敛取代和正向选择位点对叶绿体蛋白结构和功能的影响,我们利用现有的x射线晶体结构数据进行了结构分析。叶绿体基因的二级结构具有适应性进化的保守特征衣原体sp。使用PHYRE2服务器预测ICE-L.Phyre2是升级到原始蛋白质同源性/类比识别引擎的[52.].使用I-TASSER服务器提供的同源建模软件预测三维(3D)结构[53.].函数信息来源于Uniprot (http://www.uniprot.org/).我们用其同源蛋白质对齐基因衣藻reinhardtii和拟南芥.使用ePlant Web服务器将非随机收敛替换和积极选择的位点绘制到预测的二级和三维结构上,以可视化功能位置[54.].
结果
光合叶绿体基因的正向选择
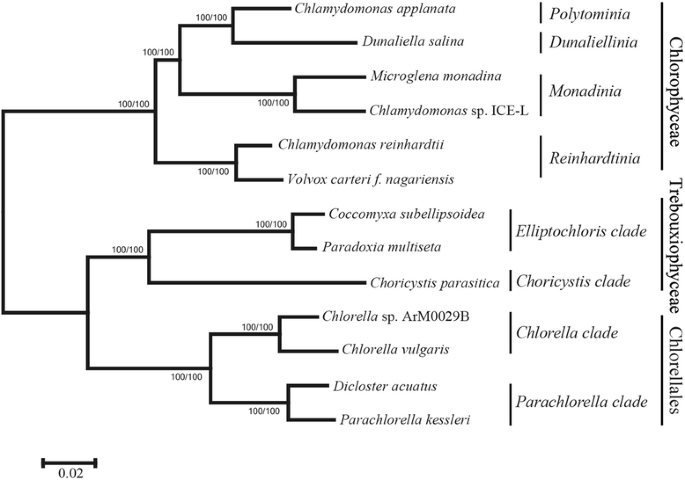
最大似然树确认衣原体(叶绿素)(叶绿素)包含多个枝条[55.那56.], 和衣原体sp. ICE-L是一个姐妹组Microglena monadina基于第1 + 2密码子位置和氨基酸数据的高bootstrap支持(100%)(图。1).发散时间分析表明衣原体ICE-L起源于二叠纪(2407 mya;95%置信区间:138.7~ 379.9Mya1:图S1)。
为了检验叶绿体蛋白编码基因的进化模式是否衣原体sp。ICE-L与极端环境适应有关,选择了在极端环境中的四个藻类进行了比较进化分析。我们首先测试了基本模型(跨站点和分支的不变Ω),发现基因特定估计值为0.00096至0.057。所有46个基因特异性ω值小于1(附加文件1:表S1)。46个基因特异性ω值的平均值为0.02999。28个光合作用基因中,ω值大于平均值的只有9个,18个遗传系统基因中,ω值大于平均值的只有12个。
采用分支模型检验,利用基因特异性数据检测阳性选择衣原体ICE-L sp。在分支模型分析中没有积极选择的证据(纠正P.-value =1 and ω < 1;额外的文件1:表S2),表明纯化选择在叶绿体蛋白编码基因中显着。同样,考虑到其他三种绿藻(Coccomyxa subellipsoideaC-169,小球藻sp。ArM0029B和Dunaliella Salina.)生活在极端环境作为前景(附加文件1:表S2)。使用基于两个功能分类(光合作用和遗传系统)的两个连接数据时,测试在任何情况下都显示了四种藻类中的任何一种阳性选择的证据(衣原体sp。冰-L,Coccomyxa subellipsoideaC-169,小球藻sp。ArM0029B和Dunaliella Salina.)(附加文件1:表S2)。
随机站点模型,忽略谱系之间的ω变化,用于识别某些网站是否是正选择的目标。在每个基因位点特异性测试阳性选择中,我们使用一对位点模型的(M8A与M8)和FDR校正所述多个LRT比较(校正P.值< 0.05)。使用贝叶斯经验贝叶斯(BEB)方法进行正向选择并没有确定具体位点,这证实了净化选择是塑造绿藻叶绿体基因进化的主要力量(补充文件)1:表S3)。此外,跨两个连接数据的站点特异性后均线ω的检查显示,几乎所有站点的Ω值几乎为零。存在ω值的一些网站超过0.5(附加文件1:图S2)暗示这些地点可能存在弱净化选择或间歇性积极选择[42.].
基因特异性数据的分支位点分析证实了正选择的证据沿着谱系导致衣原体sp。冰-L,Dunaliella Salina.和小球藻sp. ArM0029B的后验概率≥0.95,使用Bayes经验Bayes (BEB)方法(表2)[46.].BEB分析鉴定出肯定选择基因:三(atpB那psaB,rbcl.) 在衣原体sp。ICE-L,三(atpA那atpB,psbC) 在Dunaliella Salina.和两个(atpE和佩塔) 在小球藻ArM0029B sp。三种基因分支部位模型的LRT(atpB那psbC和psbD) 在Coccomyxa subellipsoidea校正后C-169在统计学上显着,但在BEB分析中没有鉴定的肯定选择(PP> 0.95)。获得了相同的结果atpB基因小球藻ArM0029B sp。分别确定了10个和19个阳性位点衣原体sp。ICE-L和Dunaliella Salina.,而在小球藻ArM0029B sp。更重要的是,所有阳性选择的基因都是光合和编码的重要光合蛋白,其对非生物应激敏感。
两个连接数据的分支站点分析确定了七个基因中阳性选择的签名(atpB那psaA那psaB那psbA那psbD那rbcl.和rpl2;共10个地点)衣原体sp. ICE-L, 12个基因(atpA那atpB那佩塔那psaA那psbC那psbD那ccsA那chlN那rpl5那rpl23.那rps4和YCF12.;总共30个网站)Dunaliella Salina.(附加文件1:表S4)。虽然基于连接数据的正选择基因的数量与基因特异性数据的数量不同,但它始终表明大多数正选择位点(9/10和23/30)都在光合基因中衣原体sp。ICE-L和Dunaliella Salina.,分别。没有证据表明阳性选择Coccomyxa subellipsoideac - 169和小球藻ArM0029B sp。可以推测,这些基于基因特异性和串联数据的差异反映了在大的串联数据与小的基因特异性数据相比,增加数据的好处和共享参数估计的成本之间的权衡。不可否认的是,串联数据分析证实了基因特异性分析的结果。
总之,利用基因特异性和级联数据进行的积极选择分析揭示了极端环境下绿藻叶绿体蛋白编码基因的适应性进化模式:它们以功能特异性和谱系特异性的方式显示,积极选择主要针对光合基因衣原体sp。ICE-L和杜氏。这些正选择的基因被用于后续的收敛分析,以发现适应进化的保守特征。
收敛演变衣原体sp。ICE-L高盐度条件
自适应收敛意味着由于类似的环境因素,两个或多个距离谱系独立地发展了类似的性状[57.].我们在两种黑凝藻藻藻藻藻之间鉴定了非random收敛和平行氨基酸取代(衣原体sp。ICE-L和Dunaliella Salina.).来自5个基因(佩塔那psbF那psbZ那rbcl.那塔布)来自四种基因的四个收敛替代品(atpB那atpI那佩塔那psaB)显示之间的显着收敛衣原体sp。ICE-L和Dunaliella Salina.(附加文件1:表S5)。七个收敛基因是光合作用,一个基因(塔布)编码延伸因子Tu负责催化氨基酰- trna (aa-tRNA)与核糖体结合。与正选择结果一致,趋同进化主要以光合基因为靶点,表现出相同的功能特异性。为了揭示更多的适应进化的保守特征,我们聚焦于非随机收敛氨基酸替代的积极选择基因。因此,三个基因(atpB那psaB,rbcl.)具有正选择和趋同进化双重特征,尽管正选择位点与趋同进化位点并不重叠(表)3.).考虑到类似的高盐度环境衣原体sp。ICE-L和Dunaliella Salina.,我们推测,对这些基因的适应性演化的保守签名与盐胁迫的适应相关。
结构和功能分析
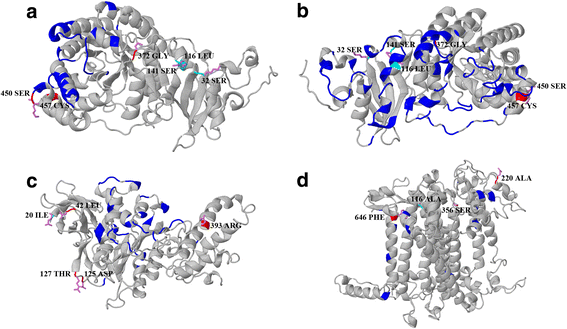
正向选择位点和非随机收敛取代都被映射到三维晶体结构上。大多数识别出正选择位点和非随机收敛取代衣原体sp. ICE-L定位于或接近关键残基和功能区域,表明许多位点具有功能相关性。在rbcl.基因,肯定选定的Ser450和半胱氨酸457接近异质二聚体界面(TRP451和职业453)在大亚基的羧基 - 末端,并且非洲收敛氨基酸取代雷116.和Ser141.是来自同源二聚体界面的一九个氨基酸(ASN115.和阿拉132.) (图。2A那B.).正面选择的网站ASP125.在atpB基因是来自α亚基相互作用界面位置ASN的五个氨基酸120.(图。2C).至于psaB基因,阳性选择的部位phe646定位于跨膜结构域(644-666位氨基酸),是辅助因子Mg中的8个氨基酸2+绑定站点他655(位置655氨基酸)。此外,肯定选择的网站ALA220的psaB基因是来自预测的碳水化合物结合位点Asn的10个氨基酸210(图。2D).
讨论
光合作用是藻类的重要能量累积过程,不同的非生物应力可能会推动光合蛋白的适应性修改。使用在极端环境中生活在极端环境中的藻类的叶绿体蛋白编码基因进行比较分析,旨在揭示与极端环境的适应性的关系。
基因特异性和连接数据的分支模型试验显示靶向致氯化体蛋白编码基因的阳性选择的显着证据,这表明强净化选择强(ω<1)。通常,功能基因是高度保守的,并且阳性选择可以仅靶向特定分支的特定位点,因此分支模型试验中的阳性选择是罕见的。基于基因特异性和级联数据的随机部位模型试验表明,通过BEB分析鉴定出没有积极选择的部位,这意味着纯化选择是植物叶绿体基因的演变的主要力。推导出两种可能的原因。一种原因是叶绿体蛋白编码基因被保守以维持光合作用,另一个原因是正选择可能在特定谱系中的某些位点上操作。
正如预期的那样,阳性选择可能针对特定谱系中的特定位点的概念通过分支位点模型检验得到了证实。在我们的分析中,只有3个位点在阳性选择下被确定小球藻sp. ArM0029B and no site onCoccomyxa subellipsoideaC-169,而大量的遗址都是这样确定的衣原体sp。ICE-L和Dunaliella Salina.在基因特异性和串联数据分析中。我们的结果表明,正向选择只针对叶绿体光合蛋白编码基因衣原体sp。ICE-L和Dunaliella Salina.谱系。
考虑到观察到的类似生理特性(耐盐)衣原体sp。ICE-L和Dunaliella Salina.,升高的盐度可能是叶绿体蛋白编码基因的适应性分子演变的动机。我们的收敛分析表明,八个会聚基因中的七个之间衣原体sp。ICE-L和Dunaliella Salina.是展示其功能特异性的光合素。为什么不同的进化模式出现在四个藻类适应极端环境中?一种可能性是光合系统的自适应演化可能涉及核编码的亚基。我们注意到叶绿体基因组在核基因组无功能无关[9.].天线复合物(核编码)经历了适应性修改,降低了光吸收效率并进一步降低了对照系统的损坏概率[58.].另一种可能的解释是,对其他非生物应激靶向基因的自适应修饰足以保持光合作用的稳态,而不需要叶绿体编码的光合亚基的适应性演变[59.那60.].
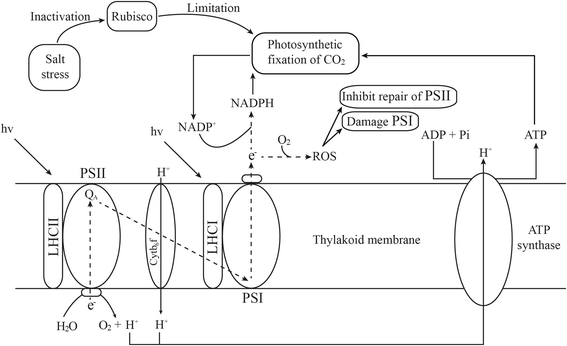
三维(3D)晶体结构分析显示了对自适应位点如何影响叶绿体光合蛋白的功能和结构的更有见解。在这里,我们专注于正面选择的基因(rbcl.那psaB和atpB)的聚合氨基酸取代衣原体ICE-L sp。的rbcl.编码Rubisco的基因是用自适应演化的保守签名鉴定,并且在我们的分析中检测到的许多适应性修改可能负责高盐度应力。Rubisco是光合作用中无机碳固定的基本酶之一和盐胁迫的主要靶标。高浓度的NaCl可能限制Rubisco的活性,这会抑制CO的固定2(图。3.)[15.那61.那62.].限制CO的光合固定2可以诱导活性氧的产生[63.].ROS主要在植物叶绿体中产生,可在盐胁迫下增强。据报道,在盐胁迫下产生的ROS降低光合速率和羧化效率,从而产生光合作用的限制[64.那65.].非随机收敛替换(SER)32.,鲁116.和Ser141.)和肯定选择的网站(Ser450和半胱氨酸457) 在rbcl.基因在同型二聚体/异二聚体界面附近,这可能有助于酶的稳定性和活性[66.].很可能是rubisco衣原体sp。ICE-L进化以恢复活性并适应非生物应力(例如高盐度)。
此外,ROS是在PSI反应中心生产的,这反过来损坏PSI [67.].保护PSI免受盐胁迫下产生的过量ROS的光损伤至关重要[68.].假设……是合理的衣原体sp. ICE-L有一些自适应修饰以增加对光损伤的抵抗力。为psaB基因,适应性积极选择位点PHE647和辅因子Mg2+绑定站点他655可能有助于保持PSI的完整性,以正常的能量转移效率。PSI反应中心多肽PsaA和PsaB结合许多电子传递元件[69.那70那71.].我们的结果表明psaB参与光养电子传输链的基因经历了适应性的进化,这可能有助于保持PSI的稳定性衣原体ICE-L sp。
我们还发现atpB叶绿体中与ATP合成相关的基因在自适应演化下(表3.).ATP合酶的β亚基atpB基因负责ATP合成的催化。正面选择的网站ASP125.在atpB基因靠近α / β亚基相互作用界面ASN120..根据现有的功能信息,这种适应性修饰可能有助于ATP合酶的活性,并提高ATP合酶活性衣原体sp. ICE-L可以满足CO的需要2固定。更具结构和功能信息对于获得更多洞察力的适应性修改至关重要atpB基因。总之,这些分子证据证明了这一点衣原体在高盐度环境下,ICE-L可能会进化以维持较高的光合速率和羧化效率,以及光合基因的适应性修饰衣原体sp. ICE-L对盐胁迫的选择压力作出反应。
注意,在经过适应性演化的基因中检测到阳性选择和收敛效果。有多种适应性策略影响自适应替代品,合理的是,在极端环境中生活在极端环境中的不同绿藻中的置换自适应取代在目前的研究中不会收敛。同样,涉及海洋哺乳动物的收敛演变的最近作品揭示了海洋哺乳动物的收敛与阳性选择之间没有显着正相关[72.].此外,还有不同类型的收敛演化,如序列收敛、功能收敛、机制收敛和结构收敛[73.].先前的一项研究表明,在基因、操纵子和功能复合物的水平上出现了强烈的收敛模式大肠杆菌[74.].我们认为,进一步的功能和结构分析,这些适应性替代衣原体sp。Ice-L将补充我们的研究结果。
结论
我们调查叶绿体光合作用来自南极绿藻的自适应机制衣原体ICE-L sp。我们的研究为正达尔文选择作用于叶绿体蛋白编码基因提供了强有力的证据衣原体sp. ICE-L遵循功能特异性和谱系特异性模式适应极端环境。我们鉴定了三个具有适应性进化保守特征的基因衣原体sp。冰-1,这些基因的自适应修饰在功能性重要的蛋白质中。我们的结果揭示了光养的组分衣原体sp。Ice-L在极端环境下展示自适应演变,高盐度可能是叶绿体水平的适应性的重要触发。应当注意,光合系统的一些亚基是编码的核基因组,通过分析叶绿体和核基因组中的所有光合基因来了解自适应策略将更有益。进一步的实验和结构分析将提供确认证据,揭示了光合体系的自适应演变衣原体ICE-L sp。
缩写
- BEB:
-
贝叶斯经验贝叶斯
- BS:
-
引导支持
- LHCS:
-
聚光复合物
- 轻轨交通:
-
似然比检验
- Phyre:
-
蛋白质同源/类比识别引擎
- PP:
-
后验概率
- ROS:
-
活性氧
- 二磷酸核酮糖羧化酶:
-
核糖糖二磷酸羧酸酶/氧化酶
参考
- 1。
Blanc G,Agarkova I,Grimwood J,Kuo A,Bruegan A,Dunigan DD,Gurnon J,Ladunga I,Lindquist E,Lucas S。极性真核微藻Coccomyxa次微征的基因组揭示了冷适应的特征。基因组Biol。2012; 13(5):1-12。
- 2。
南极海冰:极端微生物的栖息地。科学。2002;295(5555):641 - 4。
- 3.
南极海冰的主要生产要素。科学。1997;276(5311):394 - 7。
- 4.
一个m,mou s,张x,zheng z,ye n,王d,张w,miaoj.脂肪酸去饱和酶基因和脂肪酸积累的表达。冰胁迫下的冰。贪婪的技术。2013; 149:77-83。
- 5。
刘C,王X,王X,Sun C.将南极衣原体适应海冰环境:转录组分析。Expealophiles。2016; 20(4):437-50。
- 6。
王志强,王志强,王志强,等。微藻光合作用对气候变化的响应。极地杂志。1989;9(7):437 - 42。
- 7。
王玉波,刘芳,张旭,张安,王波,郑智,孙超,苗杰。南极冰微藻衣藻属ICE- l类囊体膜组成及其对低温环境胁迫的响应。英国生物学协会。2017年,97(6):1241 - 49。
- 8。
新一代细胞器基因组学:高通量技术在分子进化研究和植物系统学中的潜力和缺陷。在:Hörandl E, Appelhans MS,编辑。植物系统学的新一代测序。维也纳:Koeltz科学图书;2015.
- 9。
黄志强,王志强,王志强,等。叶绿体光合作用的分子系统学研究进展。植物科学进展。2011;16(12):645-55。
- 10。
De Koning AP,龙骨PJ。寄生绿藻幽灵孢子SP的完全塑性基因组序列。高度减少和结构。BMC BIOL。2006; 4(1):12。
- 11.
Maul Je,Lilly Jw,Cui L,Miller W,Harris EH,Stern DB。衣原体Reinhardtii血浆染色体在重复海洋中的基因群。植物细胞。2002; 14(11):2659-79。
- 12.
牟松,张欣,叶宁,董敏,梁春,梁强,苗军,徐东,郑志强。南极微藻LhcSR基因的克隆和表达分析。极端微生物。2012;16(2):193 - 203。
- 13。
唐GQ,NoviTzky WP,Carol Griffin H,Huber Sc,杜威Re。大豆的油酸去饱和酶:通过差异稳定性和磷酸化调节的证据。工厂J. 2005; 44(3):433-46。
- 14。
Devos N, Ingouff M, Loppes R, Matagne RF。RUBISCO对低温的适应:嗜冷和嗜中单细胞藻类的比较研究。J Phycol。1998;34(4):655 - 60。
- 15.
ZISKA LH,Seamann JR,Dejong TM。盐度诱导沉淀在Prunus Salicina的光合作用局限,落叶树种类。植物理性。1990; 93(3):864-70。
- 16。
关键词:紫菜,紫菜,胞囊腺藻,繁殖体,光合作用,DNA足底。2007;225(6):1505 - 16。
- 17。
紫外光照射下南极褐藻紫囊藻(Ascoseira mirabilis)配子的DNA损伤和修复。南国生态。2007;32(8):917 - 26所示。
- 18。
冷却:嗜冷藻类的进化和多样化,以衣藻目为重点。极地杂志。2017;(6):1169 - 84。
- 19。
Bascuñán-Godoy L, Sanhueza C, Cuba M, Zuñiga GE, Corcuera LJ, Bravo LA。与安第斯生态型的Colobanthus quitensis Kunt Bartl (Cariophyllaceae)相比,冷驯化通过促进南极地区更高的光化学量子产量和更有效的PSII恢复来限制低温诱导的光抑制。植物学报。2012;12(1):1 - 15。
- 20.
引用本文:王志强,王志强,王志强。不同深度梯度南极海藻的光合特性及其对紫外线胁迫的耐受性。极地杂志。2013;36(9):1319 - 32。
- 21.
Hünkenm,更难的J,Kirst G.南极冰的果皮细菌抗冰淇淋Amphiprora Kufferathii Manguin Cleave在藻类光合作用期间产生的过氧化氢。植物BIOL。2008; 10(4):519-26。
- 22.
曲燕,赵华,韩宁,周刚,宋刚,高斌,田胜,张军,张瑞,孟X.青藏高原地面山雀对高海拔生活的适应。Nat Commun。2013;4:2701
- 23.
田R,王Z,NIU X,周K,徐S,杨G.潜水期间依锡的缺氧耐受的进化遗传学。基因组Biol Evol。2016; 8(3):827-39。
- 24.
王y,杨l,周k,张y,song z,他s。适应西藏高原的证据从藏来的腰围转录om推断出来。基因组Biol Evol。2015; 7(11):2970-82。
- 25.
Raven JA, Colmer TD。边界上的生命:土壤-流体界面的光合作用。以苔藓为中心的综合研究。中国生物医学工程学报。2016;67(6):1613-23。
- 26.
关键词:低光环境,叶绿体基因组,生物多样性,生物多样性,生物多样性中国生物医学工程学报,2016,28(9):1349 - 1351。
- 27.
MA T,Wang J,周G,Yue Z,Hu Q,Chen Y,Liu B,秋Q,王Z,张J。基因组洞察沙漠杨树的盐适应。NAT Communce。2013; 4:2797。
- 28。
南极陆生和淡水藻类的分离和培养1。Phycologia。1964;4(1):43-51。
- 29。
Ahn J-W,Hwangbo K,Lee Sy,Choi H-G,Park Y-I,Liu Jr,Jeong W-J。一种新的生物柴油生产的北极小球藻物种。贪婪的技术。2012; 125:340-3。
- 30.
张志强,张志强,张志强,等。绿藻科杜氏藻(Dunaliella Teodoresco)的历史、分布和生境[J]].见:杜氏藻:科学出版社;2009.1-13页。
- 31.
Provasoli L.培养海藻的培养基和前景。在:Watanabe A,Hattori R,编辑。文化和藻类系列。普通话会议议会。1966年9月12日至15日。63-75。
- 32。
Bankevich A, Nurk S, Antipov D, Gurevich AA, Dvorkin M, Kulikov AS, Lesin VM, Nikolenko SI, Pham S, Prjibelski AD。一个新的基因组组装算法及其在单细胞测序中的应用。中国生物医学工程学报。2012;19(5):455-77。
- 33。
altschul sf,madden tl,schaffer aa,张俊,张z,米勒w,lipman dj。Papped Blast和Psi-Blast:新一代蛋白质数据库搜索程序。核酸RES。1997年; 25(17):3389-402。
- 34。
Wyman SK, Jansen RK, Boore JL。用DOGMA自动注释细胞器基因组。生物信息学,2004;20(17):3252 - 5。
- 35。
Edgar Rc。肌肉:高精度和高吞吐量的多个序列对齐。核酸RES。2004; 32(5):1792-7。
- 36。
Löytynojaa,Goldman N.一种逐渐与插入序列的逐次对准的算法。Proc Natl Acad Sci U S A. 2005; 102(30):10557-62。
- 37。
关键词:系统发育分析,序列分析,保守序列中国生物医学工程学报。2000;17(4):540-52。
- 38。
redelings b.估算正面选择时擦除误差因对齐歧义。mol Biol Evol。2014; 31(8):1979-93。
- 39。
Stamatakis a . RAxML版本8:系统发育分析和大系统发育后期分析的工具。生物信息学。2014;30(9):1312 - 3。
- 40.
Breinholt JW,Kawahara Ay。Phylotransfriptomics:饱和的第三密码子位置基于下一代数据彻底影响树木的估计。基因组Biol Evol。2013; 5(11):2082-92。
- 41.
王志强,王志强。分子进化与系统发育。纽约:牛津大学出版社;2000.
- 42.
有丝分裂基因组进化的适应模式与海龟甲壳鳞甲的损失有关。生物医学进展。2017;34(10):2522-36。
- 43.
杨志强,杨志强,杨志强。基因插入、缺失和比对误差对阳性选择分支位点检验的影响。中国生物医学工程学报。2010;27(10):2257-67。
- 44.
杨志。PAML 4:最大似然法的系统发育分析。中国生物医学工程学报。2007;24(8):1586-91。
- 45.
Storey JD, Tibshirani R.全基因组研究的统计学意义中国科学(d辑:地球科学)2003;10(16):940 - 5。
- 46.
张建军,杨志强。一种改进的分枝位点似然法在分子水平上检测阳性选择。Mol.Biol.Evol。2005; 22(12): 2472 - 9。
- 47.
张建军,张建军。基于氨基酸序列水平的收敛性和并行进化检测。Mol.Biol.Evol。1997; 14(5): 527 - 36。
- 48.
Cox CJ,Foster Pg。绿色植物叶绿体的20状态氨基酸替代模型。mol phylocyet evol。2013; 68(2):218-20。
- 49.
Zou Z,张J.是蛋白质演进的收敛和平行氨基酸取代比中立期望更普遍吗?Mol.Biol.Evol。2015; 32(8):2085-96。
- 50.
刘永强,刘永强,邓杰,杜根,范埃尔克,乔希。海洋哺乳动物基因组的趋同进化。47 Nat麝猫。2015;(3):272 - 5。
- 51.
Thomas GWC, Hahn MW。确定从基因组数据检测自适应收敛的零模型:使用回声定位哺乳动物的案例研究。Mol.Biol.Evol。2015年,32(5):1232 - 6。
- 52.
Kelley LA, Sternberg MJ。web上的蛋白质结构预测:使用Phyre服务器的一个案例研究。Nat Protoc。2009;4(3):363 - 71。
- 53.
Zhang Y. i-Tasser服务器用于蛋白质3D结构预测。BMC生物信息学。2008; 9(1):1-8。
- 54.
Fucile G,Di Biads D,Nahal H,La G,Khodabandeh S,Chen Y,Easley K,Christendat D,Kelley L,Provart NJ。EPLANT和3D数据显示主动:万维网上的集成系统生物学。Plos一个。2011; 6(1):E15237。
- 55.
Lemieux C,Vincent AT,Labarre A,Otis C,Turmel M.叶绿素绿藻的叶绿体系统分析鉴定了一种新的血管素塞(叶绿素)。BMC EVOL BIOL。2015; 15(1):264。
- 56。
王志强,王志强,王志强,等。基于分子系统学和叶绿体超微结构的单胞菌(Gloeomonas, Volvocales,藻类科)的进化起源。J Phycol。2010;46(1):195 - 201。
- 57。
Parker J, Tsagkogeorga G, Cotton JA, Liu Y, Provero P, Stupka E, Rossiter SJ。回声哺乳动物趋同进化的全基因组特征。大自然。2013;502(7470):228 - 31所示。
- 58。
Alboresi A,Ballottari M,Hienerwadel R,GiacoCetti Gm,Morosinotto T.天线复合物保护照片I从PhotoNibition。BMC植物BIOL。2009; 9(1):1-14。
- 59。
Dolhi JM,Maxwell DP,Morgan-Kiss RM。南极衣原体罗琅会:一种用于光合作用的冷适应的新兴模型。Expealophiles。2013; 17(5):711-22。
- 60。
Hirooka S,Hirose Y,Kanesaki Y,Higuchi S,Fujiwara T,Onuma R,Era A,Ohbayashi R,Uzuka A,Nozaki H.嗜酸性绿藻基因组提供了适应酸性环境的见解。Proc Natl Acad Sci U S A. 2017; 114(39):E8304-13。
- 61。
Parry MA, Andralojc P, Khan S, Lea PJ, Keys AJ。Rubisco活性:干旱胁迫的影响。AnnBot。2002年,89(7):833 - 9。
- 62。
鲁克,曹湾,冯X,何y,江D.耐盐和敏感大豆品种的光合反应。Speckynthetica。2009; 47(3):381-7。
- 63。
叶绿体中的水循环:活性氧的清除和过量光子的耗散。植物学报。1999;50(1):601-39。
- 64.
Neals PJ,Melis A.盐度 - 胁迫增强了衣原体中光合作用的光凝结。J植物理性。1989; 134(5):619-22。
- 65.
Murata N,Takahashi S,Nishiyama Y,Allakhverdiev Si。在环境压力下照相系统的光抑制。BBA-Bioenergetics。2007; 1767(6):414-21。
- 66.
洪S,Spreitzer RJ。补充桶底部的替代物影响核苷酸 - 双磷酸羧酶/氧酶的催化和稳定性。J Biol Chem。1997年; 272(17):11114-7。
- 67.
光系统I的反应中心亚基psaB基因产物的降解是在光系统I的光抑制过程中引起的:可能是活性氧的参与。植物科学。1996;115(2):157 - 64。
- 68.
李志刚,李志刚,李志刚,等。植物光系统的光抑制研究进展[j] .植物生理学报,2011;142(1):56-64。
- 69.
Rüdigerw.叶绿素B的生物合成和叶绿素循环。Photosynth Res。2002; 74(2):187-93。
- 70.
Lucińskir,jackowski g。光系统II的颜料结合蛋白的结构,功能和降解。Acta Biochim Pol。2006; 53(4):693-708。
- 71.
Green B,Durnford D.含氧光合作用的叶绿素类蛋白蛋白。Annu Rev植物植物植物Mol Biol。1996; 47(1):685-714。
- 72.
周旭,Seim I, Gladyshev VN。海洋哺乳动物的趋同进化与共同基因的不同替换有关。Sci众议员2015;5:16550。
- 73.
杜利特尔射频。趋同进化:需要明确。生物化学学报。1994;19(1):15-8。
- 74.
Titaillon O,Rodríguez-verdugo A,Gaut RL,McDonald P,Bennett AF,Long Ad,Gaut BS。自适应融合的分子多样性。科学。2012; 335(6067):457-61。
- 75.
张志军,安敏,顾智,苗军,钟波。南极海冰藻类衣原体SP..ICE-L揭示了叶绿体进化的适应模式。FigShare。2017.https://figshare.com/s/8efff1838bb4a25852eb..
致谢
我们感谢Zou和Jianzhi Zhang获得趋于致命阅读和英语编辑的收敛演变分析,以及Harold Zakon。我们感谢两个匿名评论者对此手稿的宝贵评论。
资金
本研究得到了中国天然科学基金(31570219),江苏省自然科学基金(BK20150971),江苏省科研重点项目(16KJA180002),江苏省六个人才峰项目(16KJA180002),江苏高等教育机构(PAPD)和清LAN项目的优先学术计划发展。
数据和材料的可用性
叶绿体蛋白编码序列衣原体sp. ICE-L可在GenBank查询,登录号为MF280291 - MF280350。FigShare存储库中有多个序列比对和系统发育树。https://figshare.com/s/8efff1838bb4a25852eb.[75.].
作者信息
从属关系
贡献
BZ构建了该项目并设计了实验。ZZ,MA,JM和ZG执行了实验,ZZ分析了数据。ZZ和BZ起草了稿件。所有作者都修订了稿件的最终版本。
通讯作者
伦理宣言
伦理批准和同意参与
不适用。
同意出版
不适用。
相互竞争的利益
提交人声明他们没有竞争利益。
出版商的注意
Springer Nature在发表地图和机构附属机构中的司法管辖权索赔方面仍然是中立的。
额外的文件
附加文件1:
表S1。个体基因的基本(M0)模型检验结果及级联数据。表S2。正确的结果P.- 在分支模型测试中的LRT value。表S3。对每个基因特异性和串联数据的位点模型检验结果。表S4。使用连接数据的分支站点模型分析结果。表S5。之间的收敛试验结果衣原体sp。ICE-L和Dunaliella Salina..图S1。发散时间分析结果。估计的分歧时间以95%的置信区间显示出95%。图S2。使用M8随机点模型估算连接数据的dN/dS。y轴表示每个位点的后验dN/dS的BEB均值估计。多克斯(341 kb)
权利和权限
开放访问本文根据创意公约署署署的条款分发了4.0国际许可证(http://creativecommons.org/licenses/by/4.0/)如果您向原始作者和源给出适当的信用,则允许在任何介质中进行不受限制的使用,分发和再现,提供指向Creative Commons许可证的链接,并指示是否进行了更改。Creative Commons公共领域奉献豁免(http://creativecommons.org/publicdomain/zero/1.0/)适用于本条提供的数据,除非另有说明。
关于这篇文章
引用这篇文章
张志强,安敏,苗军。等等。南极海冰藻衣原体sp. ICE-L为叶绿体进化的适应模式提供了见解.BMC植物BIOL.18,53(2018)。https://doi.org/10.1186/s12870-018-1273-x
已收到:
公认:
发表:
关键词
- 南极冰藻
- 积极选择
- 光合作用
- 收敛演变